di Giulia Campli
Metaforicamente, questa lente di ingrandimento esiste davvero e consiste nella tecnica di analisi dell’eDNA, dove “e” costituisce l’abbreviativo di “environmental”, termine inglese per “ambientale”.
Tutti gli animali rilasciano nell’ambiente, tramite pelle, escrezioni, uova, delle piccole tracce di DNA, molecola essenziale per la vita che contiene codificate tutte le informazioni peculiari di una specie. Raccogliendo queste molecole, è quindi possibile risalire alla presenza dell’organismo a cui appartengono e stimare la composizione della comunità del luogo in cui si è effettuato il campionamento.
Come vengono realizzati questi studi nella pratica?
Prima di tutto bisogna reperire il materiale biologico, tramite una fase di campionamento. La matrice ambientale viene prelevata e filtrata, tramite attrezzature specifiche rispetto all’ambiente in cui ci si trova. Decidere con attenzione dove si campiona e quando, in relazione allo scopo della nostra analisi, è fondamentale, in quanto l’eDNA si trova in concentrazioni piccolissime insieme ad una grande quantità di altre molecole. Inoltre, se si è interessati in particolar modo ad una specie o un gruppo di specie imparentate tra di loro, il nostro eDNA target rappresenterà una minima parte di tutto l’eDNA raccolto e questa dipenderà molto da diversi fattori, come la grandezza, la diffusione e la biologia della specie target.
L’eDNA è anche facilmente esposto al rischio di degradazione, che ne può diminuire ulteriormente la quantità.
La seconda fase avviene in un laboratorio e, proprio in ragione della rarità dell’eDNA, è importante avere a disposizione delle sequenze disegnate appositamente per “vedere” la porzione del DNA della nostra specie di interesse, che la rende unica e discriminabile da tutte le altre molecole di DNA. Tramite queste sequenze ad hoc è possibile amplificare il DNA di interesse per quantificarlo.
Successivamente il DNA viene sequenziato grazie alle tecnologie di nuova generazione: la sequenza di ogni molecola viene letta in ognuna delle singole componenti e resa disponibile per l’analisi dati. Infine, tramite strumenti di informatica applicata alla biologia, le molecole di DNA sequenziate vengono quantificate e confrontate con un database che costituisce una libreria di sequenze di tutte le specie, in modo da poter abbinare quelle derivanti dallo studio con quelle di referenza che sono disponibili. Adesso abbiamo identificato e stimato quali specie ci sono nell’ambiente di campionamento!
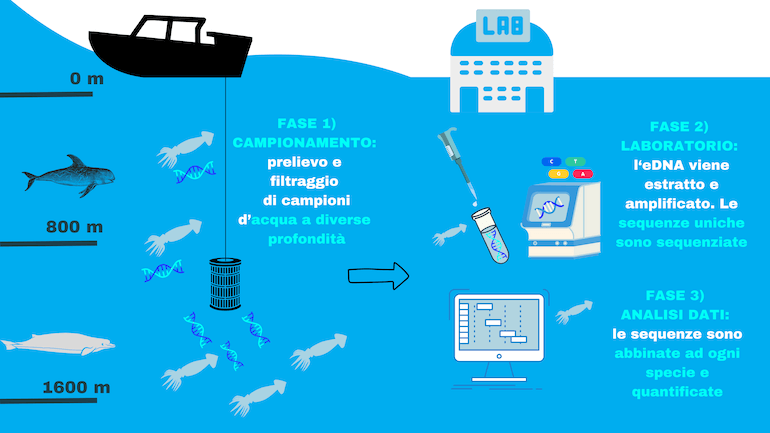
Esempio di caso studio con tecnica di eDNA: i campioni di acqua sono prelevati a diverse altezze di profondità, sia nel territorio di caccia del grampo (non piu’ di 800 m) che in quello dello zifio (fino ad un massimo di 1600 m). In laboratorio, l’eDNA è estratto e le sequenze uniche per le specie di cefalopodi sono amplificate e lette. Al computer, ad ogni sequenza viene abbinata la rispettiva specie di appartenenza, grazie ad un database. © G. Campli-MeRiS Mediterraneo Ricerca e Sviluppo.
Avendo effettuato il nostro esperimento possiamo quantificare la varietà di specie, cioè la biodiversità, e dedurre di conseguenza lo stato di salute del posto.
Oltre al monitoraggio, un altro obiettivo può essere più indirizzato ad esplorare nuovi ambienti e scoprire chi vi abita, in questo modo è possibile sia rivelare i movimenti di una specie rara ed elusiva oppure monitorare l’espansione di specie invasive, oppure addirittura osservare nuove specie mai descritte prima.
In un recente studio pubblicato sull’illustre giornale Science, Visser e colleghi hanno provato a rispondere ad una domanda ancora più complessa: è possibile usare l’eDNA per ricostruire le strategie di predazione di due specie di cetacei, il Grampo (Grampus griseus) e lo Zifio (Ziphius cavirostris)? Dunque, i ricercatori hanno registrato i suoni emessi durante le immersioni di caccia di animali etichettati individualmente. Questi dati acustici sono stati combinati con campionamenti di eDNA a diverse altezze nella colonna d’acqua, fino a 1600 m di profondità, a largo delle isole Azzorre (Portogallo). Le due diverse specie mostrano chiaramente un territorio di caccia separato, in quanto il grampo caccia in prossimità della costa, a un massimo di 600 m di profondità, mentre lo zifio si allontana di piu’ dalla costa e si immerge superando anche i 1500 m.
L’analisi di eDNA aveva lo scopo di descrivere la distribuzione di decine di diverse specie di cefalopodi, ovvero molluschi come i totani, che costituiscono la componente principale della dieta di molti cetacei. I dati di eDNA hanno quindi rivelato che, nonostante i territori di caccia siano differenti, il grampo e lo zifio non predano specie di prede diverse, in quanto una proporzione significativa di specie di cefalopodi è stata rilevata in entrambi i territori di caccia.
I ricercatori hanno quindi ipotizzato che lo sforzo energetico compiuto dallo zifio per immergersi cosi’ tanto, sia bilanciato dal fatto che a grandi profondità abbia la possibilità di nutrirsi di prede più adulte e quindi più grandi, dal contenuto energetico maggiore, compiendo un numero di tentativi di caccia minore rispetto a quelli del grampo.
Le profondità marine sono irraggiungibili tramite le tecniche di avvistamento tradizionali e poco accessibili per essere esplorate. Studiare come funzionano gli ecosistemi delle grandi profondità è importante per comprendere meglio quale sia l’impatto che il cambiamento climatico e le attività umane stiano avendo su di essi.
La flessibilità e non invasività e limitato impiego di risorse dell’analisi dell’eDNA si dimostrano dei grandi vantaggi per questa tipologia di investigazioni.
Referenze
Ruppert, K.M., Kline, R.J., Rahman, M.S., 2019. Past, present, and future perspectives of environmental DNA (eDNA) metabarcoding: A systematic review in methods, monitoring, and applications of global eDNA. Glob. Ecol. Conserv. 17, e00547. https://doi.org/10.1016/j.gecco.2019.e00547
Suarez-Bregua, P., Álvarez-González, M., Parsons, K.M., Rotllant, J., Pierce, G.J., Saavedra, C., 2022. Environmental DNA (eDNA) for monitoring marine mammals: Challenges and opportunities. Front. Mar. Sci. 9.
Visser, F., Merten, V.J., Bayer, T., Oudejans, M.G., de Jonge, D.S.W., Puebla, O., Reusch, T.B.H., Fuss, J., Hoving, H.J.T., 2021. Deep-sea predator niche segregation revealed by combined cetacean biologging and eDNA analysis of cephalopod prey. Sci. Adv. 7, eabf5908.
https://doi.org/10.1126/sciadv.abf5908
riproduzione consentita con link a originale e citazione fonte: rivistanatura.com








